网站首页健康养生 >正文
越来越多的证据表明肠道微生物群与宏基因组(MWAS)推断的多种疾病之间存在关联,表明微生物群是控制这些疾病最有前途和最有效的策略之一。然而,从高维数据推断因果关系和强关联性非常具有挑战性,导致宏基因组研究之间因果微生物识别的一致性较低。
尽管为了有效控制使人类微生物群变得复杂且高度可变的众多混杂辅助因子已经付出了巨大的努力,但在横断面研究中考虑个体异质性时仍有很长的路要走。
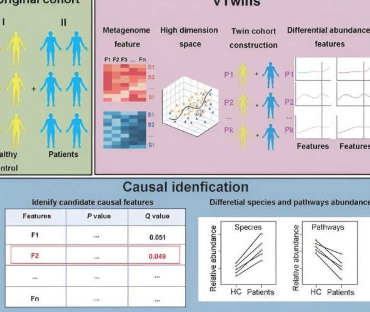
在中国科学院北京基因组研究所、中国国家生物信息中心中国科学院基因组科学与信息重点实验室于康教授领导的一项新研究中,研究人员团队开发了一种开放获取工具“虚拟双胞胎”(VTwins),它显着提高了从复杂的宏基因组数据中识别致病微生物的能力。
该研究发表在《科学通报》杂志上。
VTwins采用的创新方法受到基因研究中模仿双胞胎样本的双胞胎研究的启发,可以完美控制高度可变的遗传背景,显着减少所需的样本量,并且往往能够成功识别致病基因变异。
研究人员选择了不同表型但匹配的分类学特征的配对样本,从原始群体中重建了一个新的“双胞胎”群体。通过这个简单的转变,VTwins能够有效地控制高度可变的宏基因组混杂因素,并在后续配对样本的统计测试中取得很高的显着性。
使用模拟和经验宏基因组数据集对VTwin进行的性能评估表明,即使样本量减少,其在识别致病特征方面也具有卓越的性能。此外,VTwins还与其他16个软件进行了基准测试,并验证了其有效性和适用性。
该工具特别擅长控制不相关的混杂特征和最小化背景噪声,这是宏基因组研究中的常见挑战。这将识别疾病相关微生物特征所需的样本量减少了10倍,使VTwins成为大数据时代高维数据分析的宝贵工具。
随着宏基因组研究不断引起人们对人类微生物群与一系列疾病之间关系的关注,VTwins等工具对于深入了解疾病发病机制至关重要。
版权说明:本站所有作品图文均由用户自行上传分享,仅供网友学习交流。若您的权利被侵害,请联系我们
相关文章:
- 2023-11-29开发两种合成分子来帮助阐明细胞功能
- 2023-11-28研究人员通过新型污染检测方法为更快更安全的T细胞治疗铺平道路
- 2023-11-27氯消毒剂在杀死医院超级细菌方面并不比水更有效
- 2023-11-27细菌储存记忆并将其世代相传
- 2023-11-27受大自然启发的飞行游泳和隧道机器人
- 2023-11-27结肠类器官产生功能性常驻巨噬细胞
- 2023-11-27小胶质细胞突变会增加阿尔茨海默病的风险
- 2023-11-27新工具Facemap可通过小鼠面部运动预测大脑活动
- 2023-11-26贻贝组织和足丝之间的动态生物界面在快速释放中发挥重要作用
- 站长推荐
- 栏目推荐
- 阅读排行
- 健康和教育密切相关新西兰需要将其更多地融入小学
- Steam现已全面支持DualShock和DualSense控制器无需购买新的Xbox控制器
- DistrictTaco希望扩大其在罗利地区的业务
- Humane的AiPin–您的新型可穿戴人工智能助手
- Microsoft365CopilotAI如何提高您的工作效率
- MicrosoftRadius云开源应用程序平台
- 生产目的FiskerPear具有透明A柱因为移动头部太困难
- 索尼Xperia5V马来西亚发布Snapdragon8Gen2SoC 8GBRAM 256GB储存空间起价RM4999
- Nissan的模块化PulsarSportbak集轿跑车 旅行车和皮卡于一体
- 新奥尔良烤肉店将在中央市场推出
